本篇文章给大家分享的是有关tagAlign格式怎么在MACS软件中的运用,小编觉得挺实用的,因此分享给大家学习,希望大家阅读完这篇文章后可以有所收获,话不多说,跟着小编一起来看看吧。
在使用macs进行peak calling时,除了输入样本对应的BAM/SAM文件之外,还可以输入BED文件。BAM文件我们都非常 熟悉,将序列比对到基因组之后就可以产生这样的文件,各个比对软件也支持输出BAM/SAM格式。这种格式的文件记录了序列的比对情况,根据这个文件可以计算出基因组上的测序深度分布,从而比较不同样本的分布进行peak calling, 那么BED文件又是怎么一回事呢?
在BAM文件中,最核心的信息是序列和基因组区域的对应关系,即那些序列比对上了基因组上的哪些区域,这个信息通过BED格式也是可以来记录的。在bedtools中也提供了bamtobed的功能,基本用法如下
bedtools bamtobed -i input.bam > out.bed
输出内容示意如下
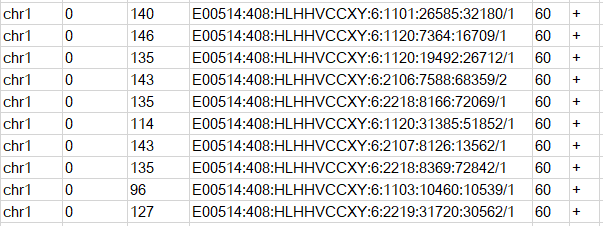
前三列表示reads比对上的染色体位置,第四列为reads的名称,第五列代表比对的质量值MAPQ,第六列代表正负链信息。
这种6列的BED文件在ENCODE被命名为tagAlign格式,详细解释参见如下链接
https://genome.ucsc.edu/FAQ/FAQformat.html#format13
对于双端测序的数据,还有一个特殊的bed格式-bedpe, 用法如下
bedtools bamtobed -i input.bam -bedpe > out.bed
内容示意如下
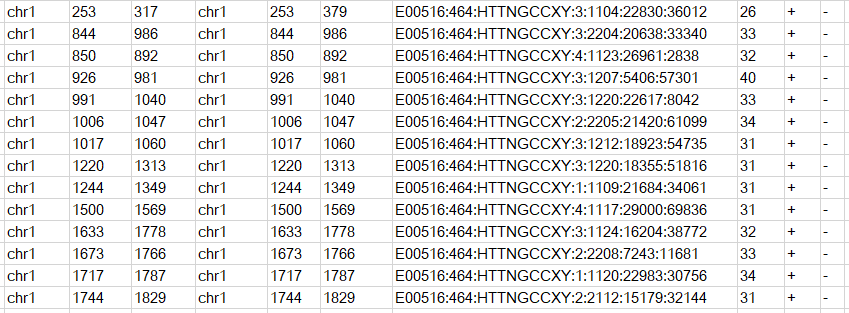
bedpe格式在一行中显示了R1和R2两个reads的比对情况,列数为10列。
对于单端序列。直接用bed格式就可以;对于双端学历,推荐用bedpe格式。这两种格式都可以称之为tagAlign,可以作为macs的输入文件,用法如下
macs2 callpeak \
-t ip.bedpe \
-c input.bedpe \
--outdir out_dir \
-n chip \
-g hstagAligen格式相比bam,文件大小会小很多,更加方便文件的读取。
以上就是tagAlign格式怎么在MACS软件中的运用,小编相信有部分知识点可能是我们日常工作会见到或用到的。希望你能通过这篇文章学到更多知识。更多详情敬请关注亿速云行业资讯频道。
免责声明:本站发布的内容(图片、视频和文字)以原创、转载和分享为主,文章观点不代表本网站立场,如果涉及侵权请联系站长邮箱:is@yisu.com进行举报,并提供相关证据,一经查实,将立刻删除涉嫌侵权内容。