жӮЁеҘҪпјҢзҷ»еҪ•еҗҺжүҚиғҪдёӢи®ўеҚ•е“ҰпјҒ
жӮЁеҘҪпјҢзҷ»еҪ•еҗҺжүҚиғҪдёӢи®ўеҚ•е“ҰпјҒ
жң¬зҜҮеҶ…е®№дё»иҰҒи®Іи§ЈвҖңrиҜӯиЁҖжҖҺд№Ҳе®һзҺ°LMжЁЎеһӢ+ж•°еҖј+еӣ еӯҗеҚҸеҸҳйҮҸвҖқпјҢж„ҹе…ҙи¶Јзҡ„жңӢеҸӢдёҚеҰЁжқҘзңӢзңӢгҖӮжң¬ж–Үд»Ӣз»Қзҡ„ж–№жі•ж“ҚдҪңз®ҖеҚ•еҝ«жҚ·пјҢе®һз”ЁжҖ§ејәгҖӮдёӢйқўе°ұи®©е°Ҹзј–жқҘеёҰеӨ§е®¶еӯҰд№ вҖңrиҜӯиЁҖжҖҺд№Ҳе®һзҺ°LMжЁЎеһӢ+ж•°еҖј+еӣ еӯҗеҚҸеҸҳйҮҸвҖқеҗ§!
第дёҖеҲ—дёәFID 第дәҢеҲ—дёәID 第дёүеҲ—д»ҘеҗҺдёәеҚҸеҸҳйҮҸпјҲжіЁж„ҸпјҢеҸӘиғҪжҳҜж•°еӯ—пјҢдёҚиғҪжҳҜеӯ—з¬ҰпјҒпјү
иҝҷйҮҢеҚҸеҸҳйҮҸж–Ү件дёәпјҡ
[dengfei@ny 03_linear_cov]$ head cov.txt
1061 1061 F 3
1062 1062 M 3
1063 1063 F 3
1064 1064 F 3
1065 1065 F 3
1066 1066 F 3
1067 1067 F 3
1068 1068 M 3
1069 1069 M 3
1070 1070 M 3
sed 's/F/1/g' cov.txt >cov2.txt
sed -i 's/M/2/g' cov2.txt
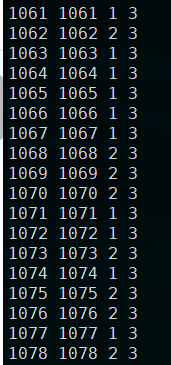
plink --file b --covar cov2.txt --write-covar --dummy-coding
з»“жһңз”ҹжҲҗпјҡ
plink.cov
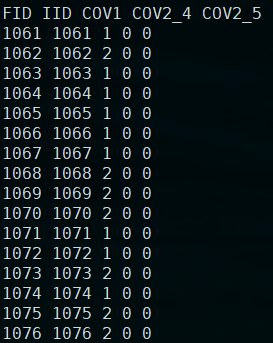
гҖҢжіЁж„ҸпјҡгҖҚиҝҷйҮҢзҡ„жҖ§еҲ«иҷҪ然жҳҜеӣ еӯҗпјҢдҪҶжҳҜе…¶еҸӘжңүдёӨдёӘж°ҙе№іпјҢд№ҹеҸҜд»Ҙе°ҶдҪңдёәиҝһз»ӯзҡ„еҸҳйҮҸпјҢи®Ўз®—ж–№жі•жҳҜдёҖж ·зҡ„гҖӮеҰӮжһңжҳҜдёүдёӘж°ҙе№ізҡ„еӣ еӯҗпјҢе°ұдёҚиғҪзӣҙжҺҘиҪ¬еҢ–дёәеҸҳйҮҸдәҶгҖӮ
гҖҢд»Јз ҒпјҡгҖҚ
plink --file b --pheno phe.txt --allow-no-sex --linear --covar plink.cov --out re --hide-covar
гҖҢж—Ҙеҝ—пјҡгҖҚ
PLINK v1.90b5.3 64-bit (21 Feb 2018) www.cog-genomics.org/plink/1.9/
(C) 2005-2018 Shaun Purcell, Christopher Chang GNU General Public License v3
Logging to re.log.
Options in effect:
--allow-no-sex
--covar plink.cov
--file b
--hide-covar
--linear
--out re
--pheno phe.txt
Note: --hide-covar flag deprecated. Use e.g. '--linear hide-covar'.
515199 MB RAM detected; reserving 257599 MB for main workspace.
.ped scan complete (for binary autoconversion).
Performing single-pass .bed write (10000 variants, 1500 people).
--file: re-temporary.bed + re-temporary.bim + re-temporary.fam written.
10000 variants loaded from .bim file.
1500 people (0 males, 0 females, 1500 ambiguous) loaded from .fam.
Ambiguous sex IDs written to re.nosex .
1500 phenotype values present after --pheno.
Using 1 thread (no multithreaded calculations invoked).
--covar: 3 covariates loaded.
Before main variant filters, 1500 founders and 0 nonfounders present.
Calculating allele frequencies... done.
10000 variants and 1500 people pass filters and QC.
Phenotype data is quantitative.
Writing linear model association results to re.assoc.linear ... done.
гҖҢз»“жһңж–Ү件пјҡгҖҚre.assoc.linear
гҖҢз»“жһңйў„и§ҲпјҡгҖҚ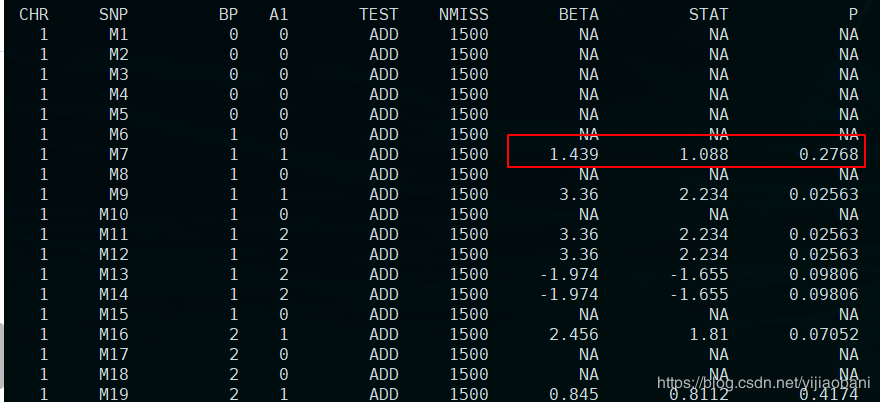
library(data.table)
geno = fread("c.raw")
geno[1:10,1:10]
phe = fread("phe.txt")
cov = fread("cov.txt")
plink = fread("plink.cov")
dd = data.frame(phe = phe$V3,cov1 = plink$COV1,cov2 = plink$COV2_4,cov3=plink$COV2_5,geno[,7:20])
head(dd)
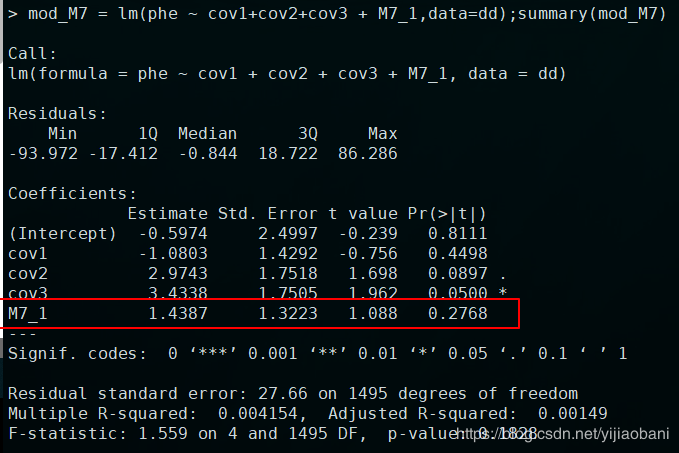
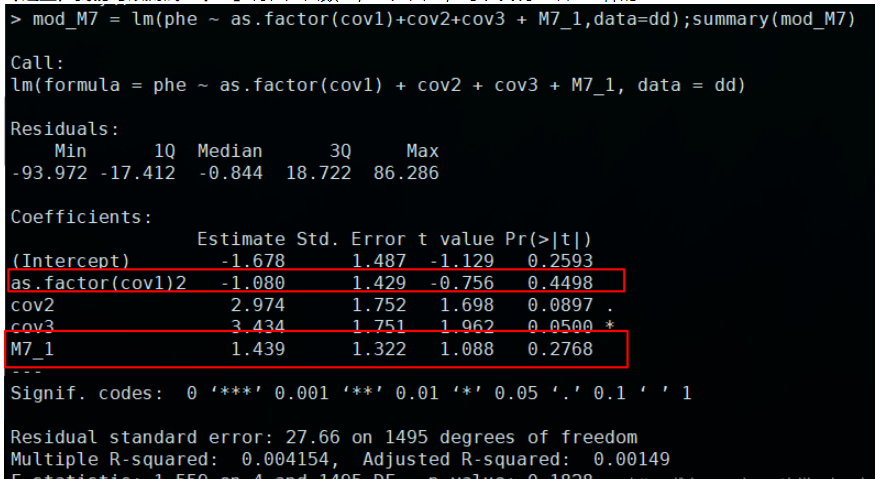
mod_M7 = lm(phe ~ cov1+cov2+cov3 + M7_1,data=dd);summary(mod_M7)
гҖҢM7еҠ дёҠеӣ еӯҗеҚҸеҸҳйҮҸз»“жһңпјҡгҖҚ
гҖҢиҝҷйҮҢпјҢжҲ‘们еҸҜд»ҘжөӢиҜ•дёҖдёӢпјҡгҖҚе°ҶжҖ§еҲ«з”ұж•°еӯ—пјҢеҸҳдёәеӣ еӯҗпјҢеҸҜд»ҘеҸ‘зҺ°з»“жһңжҳҜдёҖж ·зҡ„пјҡ
еҲ°жӯӨпјҢзӣёдҝЎеӨ§е®¶еҜ№вҖңrиҜӯиЁҖжҖҺд№Ҳе®һзҺ°LMжЁЎеһӢ+ж•°еҖј+еӣ еӯҗеҚҸеҸҳйҮҸвҖқжңүдәҶжӣҙж·ұзҡ„дәҶи§ЈпјҢдёҚеҰЁжқҘе®һйҷ…ж“ҚдҪңдёҖз•Әеҗ§пјҒиҝҷйҮҢжҳҜдәҝйҖҹдә‘зҪ‘з«ҷпјҢжӣҙеӨҡзӣёе…іеҶ…е®№еҸҜд»Ҙиҝӣе…Ҙзӣёе…ійў‘йҒ“иҝӣиЎҢжҹҘиҜўпјҢе…іжіЁжҲ‘们пјҢ继з»ӯеӯҰд№ пјҒ
е…ҚиҙЈеЈ°жҳҺпјҡжң¬з«ҷеҸ‘еёғзҡ„еҶ…е®№пјҲеӣҫзүҮгҖҒи§Ҷйў‘е’Ңж–Үеӯ—пјүд»ҘеҺҹеҲӣгҖҒиҪ¬иҪҪе’ҢеҲҶдә«дёәдё»пјҢж–Үз« и§ӮзӮ№дёҚд»ЈиЎЁжң¬зҪ‘з«ҷз«ӢеңәпјҢеҰӮжһңж¶үеҸҠдҫөжқғиҜ·иҒ”зі»з«ҷй•ҝйӮ®з®ұпјҡis@yisu.comиҝӣиЎҢдёҫжҠҘпјҢ并жҸҗдҫӣзӣёе…іиҜҒжҚ®пјҢдёҖз»ҸжҹҘе®һпјҢе°Ҷз«ӢеҲ»еҲ йҷӨж¶үе«ҢдҫөжқғеҶ…е®№гҖӮ